
資料不外流,分析環境受控
推動跨領域合作與共享,建立社群信任
研究結果經嚴格審查,保護隱私與社會利益

資料留在平台,但研究可以進行。


HARBOR 提供現代化的分析工具,協助研究者快速開始研究:
HARBOR 協助醫療資料進入國際通用格式,使跨院研究成為可能。
包括:
標準化讓研究能跨機構運作,而不需真的交換資料。


為確保資料安全,我們採用國際 TRE 標準:
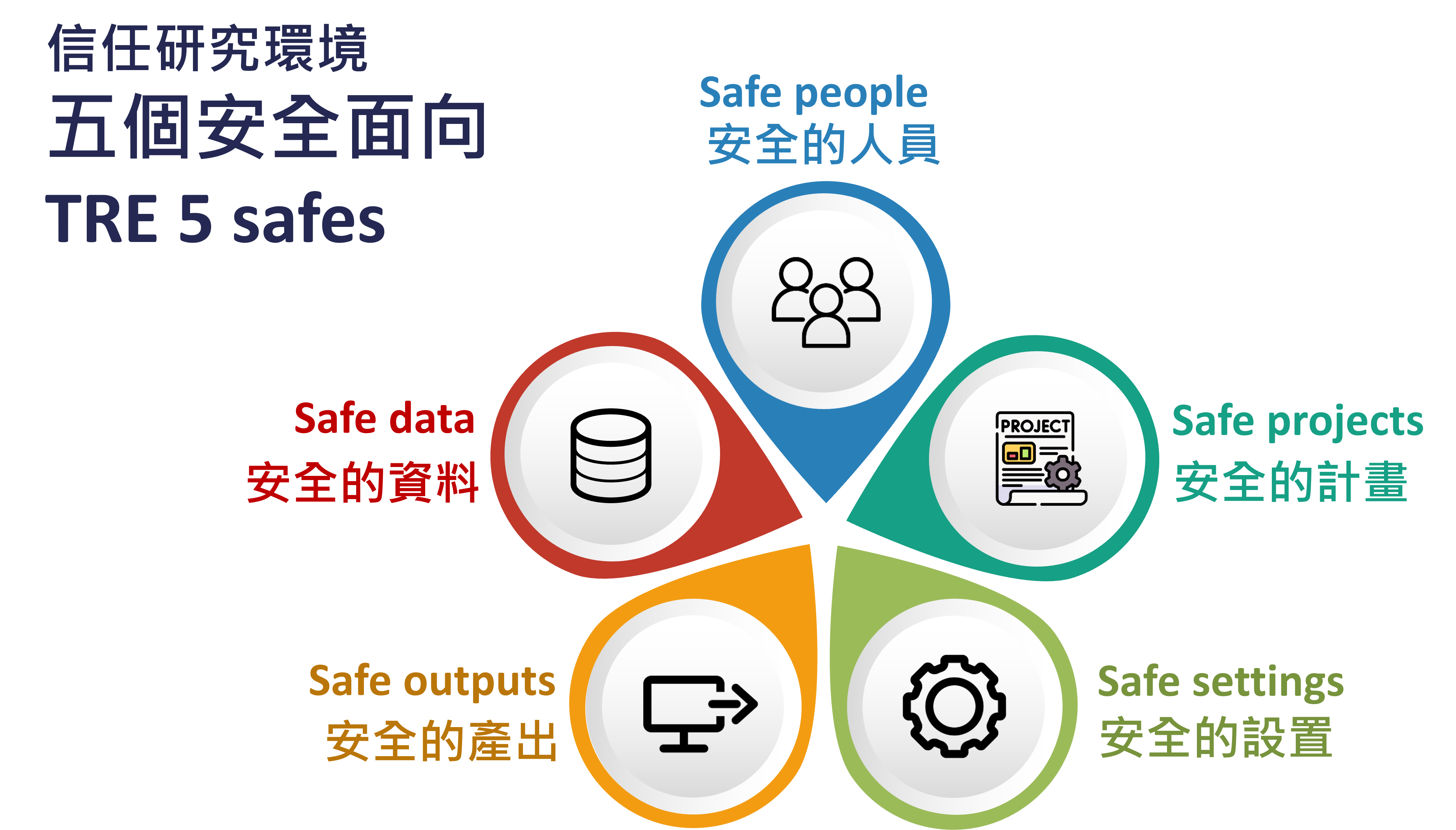
HARBOR 嚴格遵循 Five Safes 原則:Safe People、Safe Projects、Safe Data、Safe Settings、Safe Outputs。
HARBOR 已完成多項示範案例:


只有受訓合格、具授權的研究人員可存取資料。
研究計畫必須合乎倫理並具社會公共利益。
資料經過去識別或匿名化處理以保護隱私。
所有分析均在安全環境中完成,資料不外流。
研究結果須經審查後方可輸出,避免再識別。
| 層級 | 資料類型 | 使用情境 |
|---|---|---|
| 公開層 | 匿名統計資料 | 開放資料、教育 |
| 受控層 | 去識別資料 | 研究、AI 訓練 |
| 高敏感層 | 基因與精神醫療資料 | 限安全環境 |
採用隱私強化技術(PETs),提升跨域資料在安全環境中的使用能力。
透明化決策,並參考國際資料治理趨勢,促進國際合作與信任。
打造研究者與社會共贏的生態系,提升信任與參與。
TRE 的使命:
讓資料安全可用,讓研究跨越邊界,讓社會建立信任。
| No. | 軟體 | 版本 | 備註 |
|---|---|---|---|
| 1 | Python | 3.12.11 | Jupyter Notebook |
| 2 | R | 4.3.3 | Jupyter Notebook |
| 3 | RStudio | 2024.09.0+375 | Jupyter Notebook |
| 4 | Julia | 1.11.5 | Jupyter Notebook |
| 5 | PLINK | v 1.9 | GWAS was conducted using PLINK v1.9(系統內建分析 BC Pipeline - GWAS case-control, GWAS quantitative trait, Allele frequencies) |
更新日期:2026.03.10
| Package | Version | Editable project location |
|---|---|---|
| aiohappyeyeballs | 2.6.1 | |
| aiohttp | 3.12.13 | |
| aiosignal | 1.3.2 | |
| alembic | 1.16.2 | |
| altair | 5.5.0 | |
| annotated-types | 0.7.0 | |
| anyio | 4.9.0 | |
| archspec | 0.2.5 | |
| argon2-cffi | 25.1.0 | |
| argon2-cffi-bindings | 21.2.0 | |
| arrow | 1.3.0 | |
| asttokens | 3.0.0 | |
| async_generator | 1.10 | |
| async-lru | 2.0.5 | |
| attrs | 25.3.0 | |
| autograd | 1.8.0 | |
| autograd-gamma | 0.5.0 | |
| babel | 2.17.0 | |
| bcjupyterimport2 | 0.1 | /bcpackages/bcjupyterimportPy |
| bcstorage | 0.1 | /bcpackages/bcstoragePy |
| beautifulsoup4 | 4.13.4 | |
| bleach | 6.2.0 | |
| blinker | 1.9.0 | |
| bokeh | 3.7.3 | |
| boltons | 25.0.0 | |
| Bottleneck | 1.5.0 | |
| Brotli | 1.1.0 | |
| cached-property | 1.5.2 | |
| certifi | 2025.6.15 | |
| certipy | 0.2.2 | |
| cffi | 1.17.1 | |
| charset-normalizer | 3.4.2 | |
| click | 8.2.1 | |
| cloudpickle | 3.1.1 | |
| colorama | 0.4.6 | |
| comm | 0.2.2 | |
| conda | 25.5.1 | |
| conda-libmamba-solver | 25.4.0 | |
| conda-package-handling | 2.4.0 | |
| conda_package_streaming | 0.11.0 | |
| contourpy | 1.3.2 | |
| cryptography | 45.0.4 | |
| cycler | 0.12.1 | |
| Cython | 3.1.2 | |
| cytoolz | 1.0.1 | |
| dask | 2025.5.1 | |
| debugpy | 1.8.14 | |
| decorator | 5.2.1 | |
| defusedxml | 0.7.1 | |
| dill | 0.4.0 | |
| distributed | 2025.5.1 | |
| distro | 1.9.0 | |
| et_xmlfile | 2.0.0 | |
| exceptiongroup | 1.3.0 | |
| executing | 2.2.0 | |
| fastjsonschema | 2.21.1 | |
| fonttools | 4.58.4 | |
| formulaic | 1.1.1 | |
| fqdn | 1.5.1 | |
| frozendict | 2.4.6 | |
| frozenlist | 1.6.0 | |
| fsspec | 2025.5.1 | |
| gitdb | 4.0.12 | |
| GitPython | 3.1.44 | |
| gmpy2 | 2.2.1 | |
| greenlet | 3.2.3 | |
| h11 | 0.16.0 | |
| h2 | 4.2.0 | |
| h5py | 3.14.0 | |
| hpack | 4.1.0 | |
| httpcore | 1.0.9 | |
| httpx | 0.28.1 | |
| hyperframe | 6.1.0 | |
| idna | 3.10 | |
| imagecodecs | 2025.3.30 | |
| imageio | 2.37.0 | |
| importlib_metadata | 8.7.0 | |
| importlib_resources | 6.5.2 | |
| interface-meta | 1.3.0 | |
| ipykernel | 6.29.5 | |
| ipympl | 0.9.7 | |
| ipython | 9.3.0 | |
| ipython_genutils | 0.2.0 | |
| ipython_pygments_lexers | 1.1.1 | |
| ipywidgets | 8.1.7 | |
| isoduration | 20.11.0 | |
| jedi | 0.19.2 | |
| Jinja2 | 3.1.6 | |
| joblib | 1.5.1 | |
| json5 | 0.12.0 | |
| jsonpatch | 1.33 | |
| jsonpointer | 3.0.0 | |
| jsonschema | 4.24.0 | |
| jsonschema-specifications | 2025.4.1 | |
| jupyter_client | 8.6.3 | |
| jupyter_core | 5.8.1 | |
| jupyter-events | 0.12.0 | |
| jupyter-lsp | 2.2.5 | |
| jupyter-pluto-proxy | 0.1.2 | |
| jupyter-rsession-proxy | 2.2.1 | |
| jupyter_server | 2.16.0 | |
| jupyter_server_mathjax | 0.2.6 | |
| jupyter_server_proxy | 4.4.0 | |
| jupyter_server_terminals | 0.5.3 | |
| jupyterhub | 5.3.0 | |
| jupyterlab | 4.2.7 | |
| jupyterlab_git | 0.51.2 | |
| jupyterlab_pygments | 0.3.0 | |
| jupyterlab_server | 2.27.3 | |
| jupyterlab_widgets | 3.0.15 | |
| kiwisolver | 1.4.8 | |
| lazy_loader | 0.4 | |
| libmambapy | 2.3.0 | |
| lifelines | 0.30.0 | |
| llvmlite | 0.44.0 | |
| locket | 1.0.0 | |
| lz4 | 4.4.4 | |
| Mako | 1.3.10 | |
| MarkupSafe | 3.0.2 | |
| matplotlib | 3.10.3 | |
| matplotlib-inline | 0.1.7 | |
| menuinst | 2.3.0 | |
| mistune | 3.1.3 | |
| mpmath | 1.3.0 | |
| msgpack | 1.1.1 | |
| multidict | 6.5.1 | |
| munkres | 1.1.4 | |
| narwhals | 1.44.0 | |
| nbclassic | 1.3.1 | |
| nbclient | 0.10.2 | |
| nbconvert | 7.16.6 | |
| nbdime | 4.0.2 | |
| nbformat | 5.10.4 | |
| nest_asyncio | 1.6.0 | |
| networkx | 3.5 | |
| notebook | 7.2.2 | |
| notebook_shim | 0.2.4 | |
| numba | 0.61.2 | |
| numexpr | 2.10.2 | |
| numpy | 2.2.6 | |
| oauthlib | 3.3.1 | |
| openpyxl | 3.1.5 | |
| overrides | 7.7.0 | |
| packaging | 25.0 | |
| pamela | 1.2.0 | |
| pandas | 2.3.0 | |
| pandocfilters | 1.5.0 | |
| parso | 0.8.4 | |
| partd | 1.4.2 | |
| patsy | 1.0.1 | |
| pexpect | 4.9.0 | |
| pickleshare | 0.7.5 | |
| pillow | 11.2.1 | |
| pip | 25.1.1 | |
| pkgutil_resolve_name | 1.3.10 | |
| platformdirs | 4.3.8 | |
| pluggy | 1.6.0 | |
| prometheus_client | 0.22.1 | |
| prompt_toolkit | 3.0.51 | |
| propcache | 0.3.1 | |
| protobuf | 5.29.3 | |
| psutil | 7.0.0 | |
| ptyprocess | 0.7.0 | |
| pure_eval | 0.2.3 | |
| py-cpuinfo | 9.0.0 | |
| pyarrow | 20.0.0 | |
| pycosat | 0.6.6 | |
| pycparser | 2.22 | |
| pydantic | 2.11.7 | |
| pydantic_core | 2.33.2 | |
| Pygments | 2.19.2 | |
| PyJWT | 2.10.1 | |
| pyparsing | 3.2.3 | |
| PySocks | 1.7.1 | |
| python-dateutil | 2.9.0.post0 | |
| python-json-logger | 2.0.7 | |
| pytz | 2025.2 | |
| PyWavelets | 1.8.0 | |
| PyYAML | 6.0.2 | |
| pyzmq | 27.0.0 | |
| referencing | 0.36.2 | |
| requests | 2.32.4 | |
| rfc3339_validator | 0.1.4 | |
| rfc3986-validator | 0.1.1 | |
| rpds-py | 0.25.1 | |
| rpy2 | 3.5.11 | |
| ruamel.yaml | 0.18.14 | |
| ruamel.yaml.clib | 0.2.8 | |
| scikit-image | 0.25.2 | |
| scikit-learn | 1.7.0 | |
| scipy | 1.15.2 | |
| seaborn | 0.13.2 | |
| Send2Trash | 1.8.3 | |
| setuptools | 80.9.0 | |
| simpervisor | 1.0.0 | |
| simplegeneric | 0.8.1 | |
| six | 1.17.0 | |
| smmap | 5.0.2 | |
| sniffio | 1.3.1 | |
| sortedcontainers | 2.4.0 | |
| soupsieve | 2.7 | |
| SQLAlchemy | 2.0.41 | |
| stack_data | 0.6.3 | |
| statsmodels | 0.14.4 | |
| sympy | 1.14.0 | |
| tableone | 0.9.5 | |
| tables | 3.10.2 | |
| tabulate | 0.9.0 | |
| tblib | 3.1.0 | |
| terminado | 0.18.1 | |
| threadpoolctl | 3.6.0 | |
| tifffile | 2025.6.11 | |
| tinycss2 | 1.4.0 | |
| tomli | 2.2.1 | |
| toolz | 1.0.0 | |
| tornado | 6.5.1 | |
| tqdm | 4.67.1 | |
| traitlets | 5.14.3 | |
| truststore | 0.10.1 | |
| types-python-dateutil | 2.9.0.20250516 | |
| typing_extensions | 4.14.0 | |
| typing-inspection | 0.4.1 | |
| typing_utils | 0.1.0 | |
| tzdata | 2025.2 | |
| tzlocal | 5.3 | |
| unicodedata2 | 16.0.0 | |
| uri-template | 1.3.0 | |
| urllib3 | 2.5.0 | |
| wcwidth | 0.2.13 | |
| webcolors | 24.11.1 | |
| webencodings | 0.5.1 | |
| websocket-client | 1.8.0 | |
| wheel | 0.45.1 | |
| widgetsnbextension | 4.0.14 | |
| wrapt | 1.17.2 | |
| xlrd | 2.0.1 | |
| xyzservices | 2025.4.0 | |
| yarl | 1.20.1 | |
| zict | 3.0.0 | |
| zipp | 3.23.0 | |
| zstandard | 0.23.0 |
| Package | Version |
|---|---|
| askpass | 1.2.1 |
| assertthat | 0.2.1 |
| backports | 1.5.0 |
| base | 4.3.3 |
| base64enc | 0.1-3 |
| BiocManager | 1.30.26 |
| BiocVersion | 3.18.1 |
| bit | 4.6.0 |
| bit64 | 4.6.0-1 |
| bitops | 1.0-9 |
| blob | 1.2.4 |
| brew | 1.0-10 |
| brio | 1.1.5 |
| broom | 1.0.8 |
| bslib | 0.9.0 |
| cachem | 1.1.0 |
| callr | 3.7.6 |
| caret | 6.0-94 |
| cellranger | 1.1.0 |
| checkmate | 2.3.2 |
| chk | 0.10.0 |
| class | 7.3-23 |
| cli | 3.6.5 |
| clipr | 0.8.0 |
| clock | 0.7.3 |
| cluster | 2.1.8.1 |
| cobalt | 4.6.0 |
| codetools | 0.2-20 |
| colorspace | 2.1-1 |
| commonmark | 1.9.5 |
| compiler | 4.3.3 |
| conflicted | 1.2.0 |
| cpp11 | 0.5.2 |
| crayon | 1.5.3 |
| credentials | 2.0.2 |
| curl | 6.2.2 |
| data.table | 1.17.6 |
| datasets | 4.3.3 |
| DBI | 1.2.3 |
| dbplyr | 2.5.0 |
| desc | 1.4.3 |
| devtools | 2.4.5 |
| diagram | 1.6.5 |
| dials | 1.4.0 |
| DiceDesign | 1.10 |
| diffobj | 0.3.6 |
| digest | 0.6.37 |
| doFuture | 1.1.1 |
| downlit | 0.4.4 |
| dplyr | 1.1.4 |
| dtplyr | 1.3.1 |
| e1071 | 1.7-16 |
| ellipsis | 0.3.2 |
| evaluate | 1.0.4 |
| fansi | 1.0.6 |
| farver | 2.1.2 |
| fastmap | 1.2.0 |
| fontawesome | 0.5.3 |
| forcats | 1.0.0 |
| foreach | 1.5.2 |
| forecast | 8.24.0 |
| foreign | 0.8-90 |
| Formula | 1.2-5 |
| fracdiff | 1.5-3 |
| fs | 1.6.6 |
| furrr | 0.3.1 |
| future | 1.58.0 |
| future.apply | 1.20.0 |
| gargle | 1.5.2 |
| gdata | 3.0.1 |
| generics | 0.1.4 |
| gert | 2.1.4 |
| ggplot2 | 3.5.2 |
| gh | 1.5.0 |
| gitcreds | 0.1.2 |
| globals | 0.18.0 |
| glue | 1.8.0 |
| gmodels | 2.19.1 |
| googledrive | 2.1.1 |
| googlesheets4 | 1.1.1 |
| gower | 1.0.1 |
| GPfit | 1.0-9 |
| graphics | 4.3.3 |
| grDevices | 4.3.3 |
| grid | 4.3.3 |
| gridExtra | 2.3 |
| gtable | 0.3.6 |
| gtools | 3.9.5 |
| hardhat | 1.4.1 |
| haven | 2.5.4 |
| here | 1.0.1 |
| hexbin | 1.28.5 |
| highr | 0.11 |
| Hmisc | 5.2-3 |
| hms | 1.1.3 |
| htmlTable | 2.4.3 |
| htmltools | 0.5.8.1 |
| htmlwidgets | 1.6.4 |
| httpuv | 1.6.15 |
| httr | 1.4.7 |
| httr2 | 1.1.2 |
| ids | 1.0.1 |
| infer | 1.0.8 |
| ini | 0.3.1 |
| ipred | 0.9-15 |
| IRdisplay | 1.1 |
| IRkernel | 1.3.2 |
| isoband | 0.2.7 |
| iterators | 1.0.14 |
| jquerylib | 0.1.4 |
| jsonlite | 2.0.0 |
| KernSmooth | 2.23-26 |
| knitr | 1.50 |
| labeling | 0.4.3 |
| labelled | 2.14.1 |
| later | 1.4.2 |
| lattice | 0.22-7 |
| lava | 1.8.1 |
| lhs | 1.2.0 |
| lifecycle | 1.0.4 |
| listenv | 0.9.1 |
| lmtest | 0.9-40 |
| lubridate | 1.9.4 |
| magrittr | 2.0.3 |
| MASS | 7.3-60.0.1 |
| MatchIt | 4.7.2 |
| Matrix | 1.6-5 |
| memoise | 2.0.1 |
| methods | 4.3.3 |
| mgcv | 1.9-3 |
| mime | 0.13 |
| miniUI | 0.1.2 |
| minqa | 1.2.8 |
| mitools | 2.4 |
| modeldata | 1.4.0 |
| modelenv | 0.2.0 |
| ModelMetrics | 1.2.2.2 |
| modelr | 0.1.11 |
| munsell | 0.5.1 |
| nlme | 3.1-168 |
| nnet | 7.3-20 |
| numDeriv | 2016.8-1.1 |
| nycflights13 | 1.0.2 |
| openssl | 2.3.3 |
| parallel | 4.3.3 |
| parallelly | 1.45.0 |
| parsnip | 1.3.2 |
| patchwork | 1.3.1 |
| pbdZMQ | 0.3-14 |
| pillar | 1.10.2 |
| pkgbuild | 1.4.8 |
| pkgconfig | 2.0.3 |
| pkgdown | 2.1.3 |
| pkgload | 1.4.0 |
| plogr | 0.2.0 |
| plyr | 1.8.9 |
| png | 0.1-8 |
| praise | 1.0.0 |
| prettyunits | 1.2.0 |
| pROC | 1.18.5 |
| processx | 3.8.6 |
| prodlim | 2025.04.28 |
| profvis | 0.4.0 |
| progress | 1.2.3 |
| progressr | 0.15.1 |
| promises | 1.3.2 |
| proxy | 0.4-27 |
| ps | 1.9.1 |
| purrr | 1.0.4 |
| quadprog | 1.5-8 |
| quantmod | 0.4.28 |
| R6 | 2.6.1 |
| ragg | 1.4.0 |
| randomForest | 4.7-1.2 |
| rappdirs | 0.3.3 |
| rbounds | 2.2 |
| rcmdcheck | 1.4.0 |
| RColorBrewer | 1.1-3 |
| Rcpp | 1.0.14 |
| RcppArmadillo | 14.4.2-1 |
| RcppProgress | 0.4.2 |
| RcppTOML | 0.2.3 |
| RCurl | 1.98-1.16 |
| readr | 2.1.5 |
| readxl | 1.4.5 |
| recipes | 1.3.1 |
| rematch | 2.0.0 |
| rematch2 | 2.1.2 |
| remotes | 2.5.0 |
| repr | 1.1.7 |
| reprex | 2.1.1 |
| reshape2 | 1.4.4 |
| reticulate | 1.42.0 |
| rlang | 1.1.6 |
| rmarkdown | 2.29 |
| RODBC | 1.3-25 |
| roxygen2 | 7.3.2 |
| rpart | 4.1.24 |
| rprojroot | 2.0.4 |
| rsample | 1.3.0 |
| RSQLite | 2.4.1 |
| rstudioapi | 0.17.1 |
| rversions | 2.1.2 |
| rvest | 1.0.4 |
| sass | 0.4.10 |
| scales | 1.4.0 |
| selectr | 0.4-2 |
| sessioninfo | 1.2.3 |
| sfd | 0.1.0 |
| shape | 1.4.6.1 |
| shiny | 1.11.0 |
| slider | 0.3.2 |
| sourcetools | 0.1.7-1 |
| sparsevctrs | 0.3.4 |
| splines | 4.3.3 |
| SQUAREM | 2021.1 |
| stats | 4.3.3 |
| stats4 | 4.3.3 |
| stringi | 1.8.7 |
| stringr | 1.5.1 |
| survey | 4.4-2 |
| survival | 3.8-3 |
| sys | 3.4.3 |
| systemfonts | 1.2.3 |
| tableone | 0.13.2 |
| tcltk | 4.3.3 |
| testthat | 3.2.3 |
| textshaping | 1.0.1 |
| tibble | 3.3.0 |
| tidymodels | 1.3.0 |
| tidyr | 1.3.1 |
| tidyselect | 1.2.1 |
| tidyverse | 2.0.0 |
| timechange | 0.3.0 |
| timeDate | 4041.110 |
| tinytex | 0.57 |
| tools | 4.3.3 |
| tseries | 0.10-58 |
| TTR | 0.24.4 |
| tune | 1.3.0 |
| tzdb | 0.5.0 |
| urca | 1.3-4 |
| urlchecker | 1.0.1 |
| usethis | 3.1.0 |
| utf8 | 1.2.6 |
| utils | 4.3.3 |
| uuid | 1.2-1 |
| vctrs | 0.6.5 |
| viridis | 0.6.5 |
| viridisLite | 0.4.2 |
| vroom | 1.6.5 |
| waldo | 0.6.1 |
| warp | 0.2.1 |
| whisker | 0.4.1 |
| withr | 3.0.2 |
| workflows | 1.2.0 |
| workflowsets | 1.1.1 |
| xfun | 0.52 |
| xml2 | 1.3.8 |
| xopen | 1.0.1 |
| xtable | 1.8-4 |
| xts | 0.14.1 |
| yaml | 2.3.10 |
| yardstick | 1.3.2 |
| zip | 2.3.3 |
| zlib | 1.0.3 |
| zlibbioc | 1.48.2 |
| zoo | 1.8-14 |